Pontifícia Universidade Católica do Rio de Janeiro - PUC-Rio
Especialização em Ciência de Dados & Analytics
Autor: Madson Aragão
Sementre: 25/1
Validar a viabilidade de classificar dados extraídos a partir de células mamárias em processos de alteração celular (benignas vs. malignas) usando técnicas clássicas de análises de dados baseadas em Python, além de iniciar o preparo do dataset para treinamento e testes de modelos de Aprendizado de Máquina. O projeto também visa explorar a relevância biológica das variáveis envolvidas e avaliar o potencial diagnóstico do modelo.
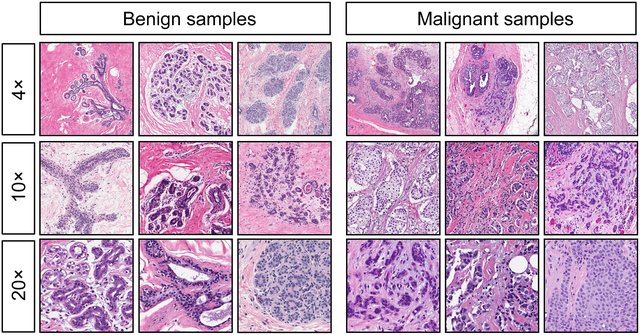
A figura abaixo ilustra, em três níveis de ampliação (4×, 10× e 20×), o contraste entre amostras benignas e amostras malignas de tumores de mama:
A figura acima apresenta um comparativo de amostras histopatológicas de tumores de mama, divididas em duas colunas principais:
- Coluna “Benign samples” - (Amostras benignas)
- Coluna “Malignant samples” - (Amostras malignas)
Cada coluna é organizada em três linhas, que correspondem a diferentes níveis de ampliação do microscópio:
| Linha | Ampliação | O que significa |
|---|---|---|
| 1 | 4× | Visão geral da arquitetura |
| 2 | 10× | Organização tecidual |
| 3 | 20× | Detalhes nucleares e citoplasmáticos |
-
Seleção e Carregamento dos Dados
- Importação do arquivo CSV contendo métricas morfológicas extraídas de imagens clínicas.
- Verificação da integridade do dataset (dimensões, tipos de variáveis, rótulos disponíveis).
- Remoção de colunas irrelevantes ou redundantes (ex.: IDs, campos vazios).
- Classificação do tipo de variável (numérica contínua, categórica ou binária) para orientar futuras transformações.
- Identificação prévia de colinearidade, valores extremos e valores faltantes.
- Registro da proporção entre amostras benignas e malignas para verificar eventual desbalanceamento.
-
Visualização Exploratória dos Dados
- Análise gráfica da distribuição das variáveis por meio de histogramas, boxplots e pairplots.
- Detecção visual de outliers e padrões por classe (benigno vs. maligno).
- Representação gráfica de correlações via heatmap para identificar redundância entre variáveis.
- Visualização/exibição (imagem ou texto) da distribuição das classes na base original e após divisão em treino/teste.
-
Pré-processamento dos Dados
- Tratamento de valores ausentes e remoção de duplicatas.
- Padronização das variáveis contínuas utilizando z-score (StandardScaler).
- Separação dos dados em conjuntos de treino e teste com proporção 75/25, utilizando
train_test_splitcomrandom_state=10para reprodutibilidade. - Verificação da distribuição de classes entre treino e teste para garantir equilíbrio.
- Armazenamento das estatísticas de normalização aplicadas na base de treino para uso posterior.
-
Transformação e Mineração de Dados
- Análise de correlações entre variáveis para identificar multicolinearidade.
- Aplicação de PCA (Análise de Componentes Principais) para reduzir dimensionalidade e observar agrupamentos de classes.
- Comparação entre variáveis para avaliar valor das informações.
- Avaliação qualitativa da separação entre classes no espaço transformado.
-
Modelo Inicial de Classificação (Extra-MVP)
- Treinamento e avaliação de um classificador K-NN (k-Nearest Neighbors) com variação de k para análise de desempenho.
- Cálculo de métricas: acurácia, precisão, recall e F1-score com base no conjunto de teste.
- Avaliação visual do desempenho via curvas de decisão, matriz de confusão e curva AUC-ROC.
- Avaliação do Matthews Correlation Coefficient (MCC), métrica robusta para avaliação de modelos de classificação binária, especialmente eficaz em cenários com classes desbalanceadas.
-
Relatório de Resultados (Extra-MVP)
- Tabela sumarizando as principais métricas por valor de k.
- Exibição da curva ROC com cálculo da AUC.
- Discussão dos erros (falsos positivos e negativos) e suas implicações clínicas.
- Indicação de configurações de k que maximizam a performance sem sobreajuste.
- (OK) Pipeline executando sem erros do início ao fim, com resultados reprodutíveis.
- (OK) Código documentado e validado em ambiente Jupyter.
- (OK) Notebook estruturado com seções claras: título, objetivos, hipóteses, análise, conclusões.
- (OK) MVP devidamente depositado, formatado e compartilhado via GitHub.
Nesta análise, utilizamos o Breast Cancer Wisconsin (Diagnostic) Dataset, um dos datasets mais consagrados em aprendizado de máquina biomédico, disponível no UCI ML Repository e outras fontes públicas.
- Tumores benignos: 357 amostras — células com arquitetura preservada, sem capacidade de metástase.
- Tumores malignos: 212 amostras — células agressivas, com invasão de tecidos e potencial metastático.
Os dados foram coletados por punção aspirativa com agulha fina (FNA) de lesões mamárias, modelando características morfológicas dos núcleos celulares via análise de imagens digitalizadas.
- Clínica Einstein – Câncer de Mama Benigno e Maligno
https://www.einstein.br/noticias/noticia/cancer-benigno-maligno - Breast Cancer: Pathogenesis and Treatments
https://www.nature.com/articles/s41392-024-02108-4 - The Size Differences of Breast Cancer and Benign Tumors Measured by Two-Dimensional Ultrasound and Contrast-Enhanced Ultrasound
https://onlinelibrary.wiley.com/doi/10.1002/jum.16449 - Distinguishing Between Benign and Malignant Breast Lesions using Diffusion Weighted Imaging and Intravoxel Incoherent Motion: A Systematic Review and Meta-Analysis
https://www.sciencedirect.com/science/article/abs/pii/S0720048X21002904
O Wisconsin Breast Cancer Dataset contém 569 amostras, cada uma com 30 variáveis morfológicas discretizadas em três escalas:
| Sufixo | Significado | Exemplos |
|---|---|---|
| _mean | Média do atributo | radius_mean, texture_mean |
| _se | Erro-padrão da média | radius_se, area_se |
| _worst | Valor extremo | perimeter_worst, concavity_worst |
- Tamanho: raio, perímetro, área
- Textura: desvio-padrão dos tons de cinza
- Irregularidade de contorno: smoothness, compactness, concavity, concave points
- Simetria e complexidade fractal do contorno
- Alta relevância clínica para diagnóstico precoce e triagem.
- Qualidade e consistência amplamente validadas.
- Desafio binário com leve desbalanceamento, ideal para métricas robustas.
- Facilita comparação com trabalhos acadêmicos prévios.
- Checagem inicial: dimensões, tipos, valores faltantes e duplicados.
- Balanceamento: proporção 357 benignos : 212 malignos, com amostragem estratificada.
- Análise de correlação: heatmap para identificar pares com correlação alta (|r| > 0.9), por exemplo,
radius_mean,perimeter_mean,area_mean. - Seleção de atributos: priorização das variáveis com sufixo
_mean, descartando_see_worstpara reduzir multicolinearidade. - Padronização: aplicação do
StandardScaler()do sklearn. - Divisão treino/teste: 75% treino · 25% teste, com
random_state=10e estratificação.
| Hipótese | Descrição |
|---|---|
| H1 | Pleomorfismo nuclear — tumores malignos exibem maior variação no radius_mean e area_mean. |
| H2 | Irregularidade de contorno — aumento do perimeter_mean refletindo formas invaginadas. |
| H3 | Agrupamento em PCA — separação clara entre benigno e maligno. |
| H4 | Performance do K-NN — distância separa amostras benignas e malignas eficientemente. |
| Variável | Descrição Técnica | Relevância Clínica/Biológica |
|---|---|---|
radius_mean |
Média do raio do núcleo | Núcleos malignos tendem a ser maiores |
texture_mean |
Desvio-padrão dos tons de cinza | Cromatina heterogênea em tumores malignos |
perimeter_mean |
Média do perímetro do contorno | Reflete tamanho e irregularidade nuclear |
area_mean |
Média da área do núcleo | Área aumentada indica maior atividade tumoral |
smoothness_mean |
Variação local do raio | Bordas irregulares típicas de células agressivas |
concavity_mean |
Profundidade média das concavidades | Concavidades refletem invaginações nucleares |
concave points_mean |
Número médio de pontos côncavos | Marcas de contornos recortados em malignidades |
symmetry_mean |
Assimetria média | Assimetria nuclear correlaciona-se ao grau de diferenciação |
fractal_dimension_mean |
Complexidade fractal do contorno | Alto valor indica desorganização estrutural extrema |
(Demais variáveis com sufixos _se e _worst estão no dataset completo.)
Embora tenha utilizado o dataset completo, foram definidas condições para a seleção de features que alimentaram meu modelo final. A principal condição foi a redução de multicollinearidade. Com base nas análises dos mapas de calor, logo foi dedicido por remover um conjunto de características (droplist_final) que eram altamente correlacionadas, com o objetivo de evitar redundância, simplificar o modelo e torná-lo mais estável.
| Etapa | Detalhe |
|---|---|
| Divisão de dados | 75% treino · 25% teste, estratificado |
| Padronização | StandardScaler() — z-score |
| Seleção de k | Teste de k = 1 a 14; k = 7 é o mais indicado |
| Modelo final | KNeighborsClassifier(n_neighbors=7) (distância Euclidiana) |
| Predito: Benigno | Predito: Maligno | |
|---|---|---|
| Real: Benigno | 89 (VN) | 2 (FP) |
| Real: Maligno | 4 (FN) | 48 (VP) |
| Métrica | Valor |
|---|---|
| Acurácia | 0.9580 |
| Matthews Correlation (MCC) | 0.9090 |
| AUC-ROC | 0.9968 |
| Precisão (Benigno/Maligno) | 0.96 / 0.96 |
| Recall (Benigno/Maligno) | 0.98 / 0.92 |
| F1-Score (Benigno/Maligno) | 0.97 / 0.94 |
- Alta sensibilidade (92%) para tumores malignos reduz falsos-negativos.
- Especificidade elevada (98%) minimiza falsos-positivos.
- MCC elevado demonstra predições confiáveis em conjunto desbalanceado, sugerindo a exclusão de overfitting.
- AUC próxima a 1 reflete poder discriminativo excepcional.
- Pipeline de pré-processamento (seleção de variáveis e normalização) foi decisivo para estabilidade e performance.
- Ajuste de limiar via
predict_probapara minimizar falsos-negativos. - Testar algoritmos com penalização assimétrica (SVM, Random Forest, XGBoost).
- Avaliar importância de features por permutação (SHAP/LIME).
- Validar em dados externos e cross-validation estratificada.
- Explorar redes neurais (CNN) e XAI para classificação direta em imagens.
A aplicação criteriosa do K-NN, com foco em seleção de atributos relevantes e pré-processamento rigoroso, atingiu acurácia de 95,8%, AUC de 0.9968 e MCC de 0.9090. O modelo mostrou-se robusto e promissor como ferramenta de triagem diagnóstica não invasiva de câncer de mama.
Este projeto faz parte das atividades acadêmicas da disciplina de Análise de Dados e Boas Práticas como parte da Especialização em Data Science & Analytics da PUC-Rio, com fins educacionais e científicos.